Durchbruch in der Tuberkuloseforschung
Erbgut des Erregers als Schlüssel für optimale Behandlung
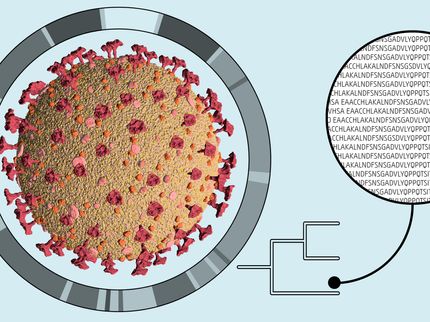
Wissenschaftlern des Forschungszentrums Borstel, des Deutschen Zentrums für Infektionsforschung, des Oxford Biomedical Research Centre und des South African National Institute for Communicable Diseases haben eine neue genetische Methode entwickelt, mit der sie nicht nur voraussagen können, gegen welche Antibiotika Resistenzen bestehen, sondern auch welche Präparate gegen den jeweiligen Tuberkulose (Tb-)-Erreger wirksam sind. Die Ergebnisse wurden am 24. Juni in der Onlineausgabe der internationalen Fachzeitschrift The Lancet Infectious Diseases veröffentlicht.
Der Nachweis von Tb-Erregern und die genaue Ermittlung von Antibiotikaresistenzen erfolgt bisher in Kulturverfahren. Diese Methode benötigt bis zu sechs Wochen, bis ein Ergebnis vorliegt. Wertvolle Zeit, die häufig eine effektive Behandlung verzögert. Zudem sind die Kulturverfahren relativ fehleranfällig. Sie müssen sehr präzise sein, um verlässliche und vergleichbare Ergebnisse zu erhalten. Solche optimalen Laborbedingungen sind jedoch insbesondere in Ländern mit hohen Tuberkuloseraten oft nicht vorhanden. Auch die in den letzten 20 Jahren eingesetzten molekulardiagnostischen Schnelltests können lediglich eine Aussage über eine begrenzte Anzahl von Mutationen und die daraus resultierenden Resistenzen treffen.
„Wir wollten einen Schritt weitergehen und therapeutische Hinweise geben, welche Kombination von Antibiotika sich zur Behandlung eines bestimmten Erregers eignen“, fasst Professor Stefan Niemann, Leiter der Forschungsgruppe Molekulare Mykobakteriologie am Forschungszentrum Borstel und Mitglied des Exzellenzclusters Entzündungsforschung, den Forschungsansatz zusammen. „Wir bewegen uns dazu von 130 Jahren Tb-Kultivierung zu einer neuen, digitalen Ära in der Mikrobiologie.“
Dazu untersuchte das Team mittels Gesamtgenomsequenzierung das Erbgut von rund 3500 Tb-Stämmen. Die Forscher konzentrierten sich dabei auf Veränderungen im Erbgut, die sie mit Antibiotikaresistenzen und -Empfindlichkeit in Verbindung bringen können. „Wir haben eine Art Lexikon für Mutationen im Erbgut der Tb-Erreger ermittelt“, erklärt Niemann. „Findet man Veränderungen im genetischen Code eines Erregers, sind bestimmte Medikamente nicht mehr wirksam und sollten daher nicht für die Therapie verwendet werden. Das ist ein enormer Fortschritt, insbesondere für die Behandlung von multiresistenten Erregern!“
Bis die Methode im praktischen Arbeitsalltag von Medizinern angewendet werden kann, dauert es aber noch etwas. Dennoch habe die Methode großes Potential, glaubt Dr. Thomas Kohl, Zweitautor der Publikation: „Auf längere Sicht ist die Genomanalyse erheblich einfacher durchzuführen und kostengünstiger als konventionelle Verfahren. Vor allem im Hinblick auf die EndTB-Strategie der WHO, die vorsieht, dass die Tuberkulose bis zum Jahr 2035 erfolgreich eliminiert werden soll, sind diese neuen diagnostischen Ansätze von großer Bedeutung.“
Tuberkulose (Tb) ist die weltweit häufigste tödliche Infektionskrankheit. Vermutlich ist etwa ein Drittel der Menschen weltweit mit dem Erreger infiziert. Bei den meisten Betroffenen bricht die Tuberkulose aber nie aus. Pro Jahr erkranken 9 Millionen Menschen an Tb – ca. 1,5 Millionen sterben an den Folgen dieser Krankheit. Insbesondere die stark zunehmenden Antibiotikaresistenzen der Erreger sind dabei ein immenses Problem. Diese verlängern die Behandlungsdauer erheblich und verursachen hohe Kosten.
Originalveröffentlichung
Walker, TM et al. (2015): Whole-genome sequencing for prediction of Mycobacterium tuberculosis drug susceptibility and resistance: a retrospective cohort study. The Lancet Infectious Diseases
Meistgelesene News
Originalveröffentlichung
Walker, TM et al. (2015): Whole-genome sequencing for prediction of Mycobacterium tuberculosis drug susceptibility and resistance: a retrospective cohort study. The Lancet Infectious Diseases
Themen
Organisationen
Weitere News aus dem Ressort Wissenschaft

Holen Sie sich die Life-Science-Branche in Ihren Posteingang
Mit dem Absenden des Formulars willigen Sie ein, dass Ihnen die LUMITOS AG den oder die oben ausgewählten Newsletter per E-Mail zusendet. Ihre Daten werden nicht an Dritte weitergegeben. Die Speicherung und Verarbeitung Ihrer Daten durch die LUMITOS AG erfolgt auf Basis unserer Datenschutzerklärung. LUMITOS darf Sie zum Zwecke der Werbung oder der Markt- und Meinungsforschung per E-Mail kontaktieren. Ihre Einwilligung können Sie jederzeit ohne Angabe von Gründen gegenüber der LUMITOS AG, Ernst-Augustin-Str. 2, 12489 Berlin oder per E-Mail unter widerruf@lumitos.com mit Wirkung für die Zukunft widerrufen. Zudem ist in jeder E-Mail ein Link zur Abbestellung des entsprechenden Newsletters enthalten.