Neue Molekülbibliothek hilft bei der systematischen Suche nach Wirkstoffen
Die Substanzbibliothek des HZB steht weltweit für die Forschung zur Verfügung
Um die Entwicklung von Medikamenten zu beschleunigen, hat das MX-Team am Helmholtz-Zentrum Berlin (HZB) mit der Drug Design Gruppe der Universität Marburg eine neue Substanzbibliothek aufgebaut. Sie besteht aus 1103 organischen Molekülen, die als Bausteine von neuen Wirkstoffen infrage kommen. Das MX-Team hat diese Bibliothek nun in Kooperation mit der FragMAX-Gruppe am MAX IV validiert. Die Substanzbibliothek des HZB steht weltweit für die Forschung zur Verfügung und spielt auch bei der Suche nach Wirkstoffen gegen SARS-CoV-19 eine Rolle.
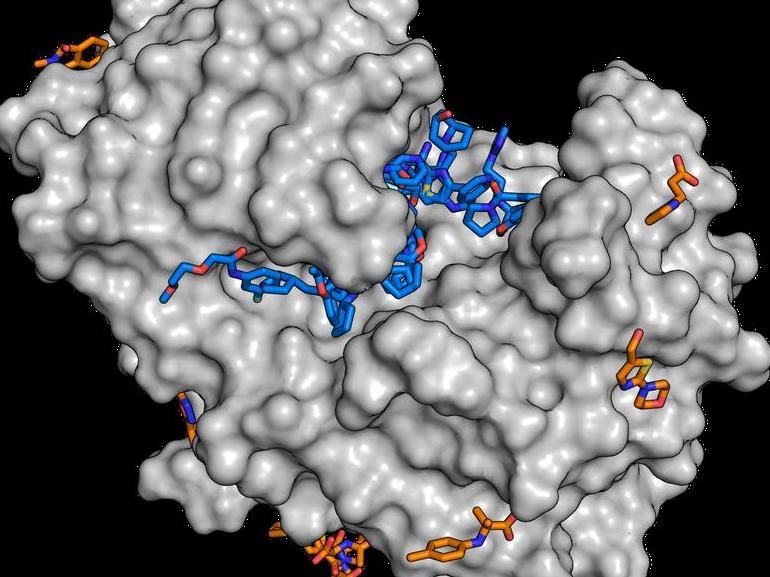
Für die Studie wurde u.a. das Enzym Endothiapepsin (grau) mit Molekülenaus der Fragmentibliothek in Kontakt gebracht. Die Analysen zeigen nun,dass zahlreiche Substanzen (blaue und orange Moleküle) an das Enzym andocken.
J. Wollenhaupt/HZB
Damit Medikamente wirken, müssen sie in der Regel an Proteine im Organismus andocken. Wie ein Schlüssel ins Schloss muss ein Teil des Wirkstoffmoleküls in Vertiefungen oder Hohlräume des Zielproteins passen. Seit einigen Jahren arbeitet das Team der Abteilung Makromolekulare Kristallographie (MX) am HZB um Dr. Manfred Weiss zusammen mit der Gruppe Drug-Design um Prof. Dr. Gerhard Klebe (Uni Marburg) daher am Aufbau von sogenannten Fragment-Bibliotheken. Sie bestehen aus kleinen organischen Molekülen (Fragmenten), mit denen sich die funktionell wichtigen Hohlräume und Vertiefungen auf der Oberfläche von Proteinen ausloten und kartieren lassen. Proteinkristalle werden dafür mit den Fragmenten getränkt und anschließend mit starkem Röntgenlicht analysiert. Dadurch lassen sich 3D-Strukturinformationen mit atomarer Auflösung ermitteln. Unter anderem kann man so herausfinden, wie gut ein bestimmtes Molekülfragment am Zielprotein andockt. Der Aufbau dieser Substanzbibliotheken fand im Rahmen des Verbrundforschungsprojekts Frag4Lead statt und wurde durch das Bundesministerium für Bildung und Forschung (BMBF) gefördert.
Das MX-Team (MX steht für Makromolekulare Kristallographie) hat nun das Design einer chemisch vielfältigen Fragmentbibliothek publiziert, die als „F2X-Universal“- Bibliothek bezeichnet wird und aus 1103 Verbindungen besteht. Aus dieser Bibliothek wurde eine repräsentative Auswahl von 96 Verbindungen extrahiert, die als F2X-Entry-Screen bezeichnet wird. Diese Auswahl ist nun im Zug dieser Publikation erfolgreich durch das MX-Team des HZB an der Röntgenquelle MAX IV in Lund, Schweden und am BESSY II getestet worden.
In der Studie verifizierten die Teams von HZB und MAX IV die Effizienz der F2X-Entry-Bibliothek durch Screening der Zielenzyme Endothiapepsin und des Aar2/Rnase-H-Komplexes. Im nächsten Schritt werden die Forscher des MX-Teams auch die gesamte Universalbibliothek zum Einsatz bringen.
"Für diese Studie haben die Berliner Fragment-Screening-Experten von HZB-BESSY II sehr eng mit dem FragMAX-Projekt-Team von MAX IV zusammen gearbeitet", sagte Dr. Uwe Müller, vom MX-Team am HZB, der sowohl die drei MX-Beamlines an BESSY II als auch die BioMAX-Beamline an MAX IV mit aufgebaut hat. "Dabei konnten beide Partner ihre eigenen Technologie-Plattformen weiterentwickeln und zur Abbildung der funktionellen Oberflächen verschiedener Proteine einsetzen. Dies ist eine hervorragende Grundlage für zukünftige Kooperationen zwischen MAX IV und dem HZB“.
Originalveröffentlichung
Originalveröffentlichung
Structure (2020): F2X-Universal and F2X-Entry: Structurally Diverse Compound Libraries for Crystallographic Fragment Screening; Jan Wollenhaupt, Alexander Metz, Tatjana Barthel, Gustavo Lima, Andreas Heine, Uwe Mueller, Gerhard Klebe, Manfred S. Weiss
Organisationen
Weitere News aus dem Ressort Wirtschaft & Finanzen

Holen Sie sich die Life-Science-Branche in Ihren Posteingang
Mit dem Absenden des Formulars willigen Sie ein, dass Ihnen die LUMITOS AG den oder die oben ausgewählten Newsletter per E-Mail zusendet. Ihre Daten werden nicht an Dritte weitergegeben. Die Speicherung und Verarbeitung Ihrer Daten durch die LUMITOS AG erfolgt auf Basis unserer Datenschutzerklärung. LUMITOS darf Sie zum Zwecke der Werbung oder der Markt- und Meinungsforschung per E-Mail kontaktieren. Ihre Einwilligung können Sie jederzeit ohne Angabe von Gründen gegenüber der LUMITOS AG, Ernst-Augustin-Str. 2, 12489 Berlin oder per E-Mail unter widerruf@lumitos.com mit Wirkung für die Zukunft widerrufen. Zudem ist in jeder E-Mail ein Link zur Abbestellung des entsprechenden Newsletters enthalten.